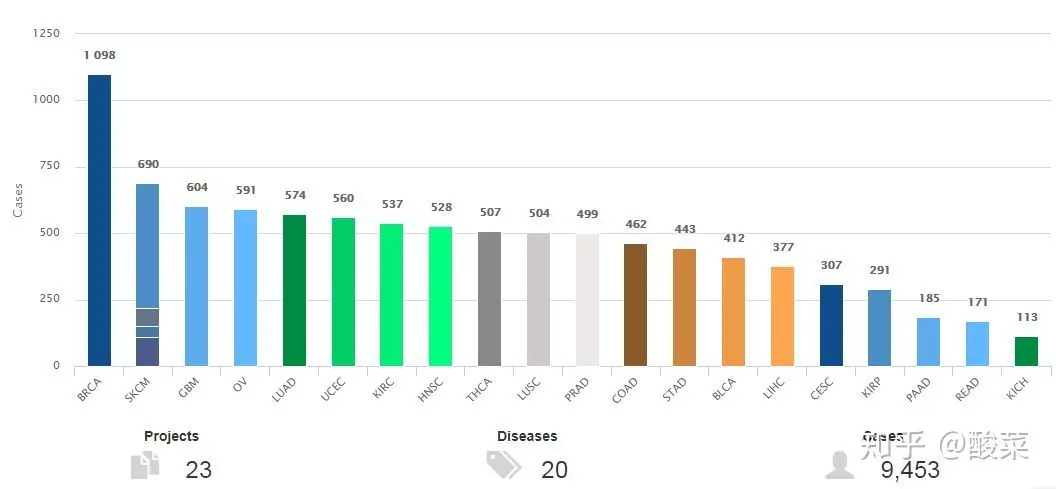
【3.9.6】20个癌种的免疫数据分析-TCIA
The Cancer Immunome Atlas (TCIA, https://tcia.at/home ) 就是基于TCGA数据开发的,不同的是TCIA只提供了20个癌种的免疫数据分析。
The Cancer Immunome Database (TCIA) provides results of comprehensive immunogenomic analyses of next generation sequencing data (NGS) data for 20 solid cancers from The Cancer Genome Atlas (TCGA) and other datasources.
看网站首页的介绍就知道,这个数据库主要是根据TCGA的二代测序数据开发出来的。这里的20个癌种,点击每个柱子进去就可以分析对应的癌种,侧边的栏目则提供一些个性化选择。
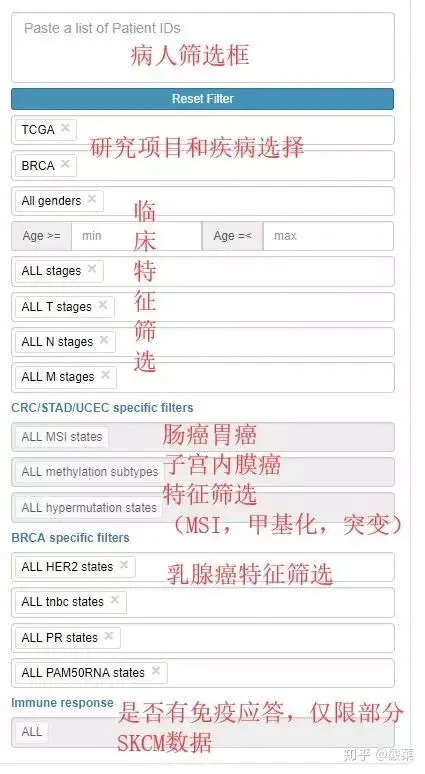
01 Patients list模块
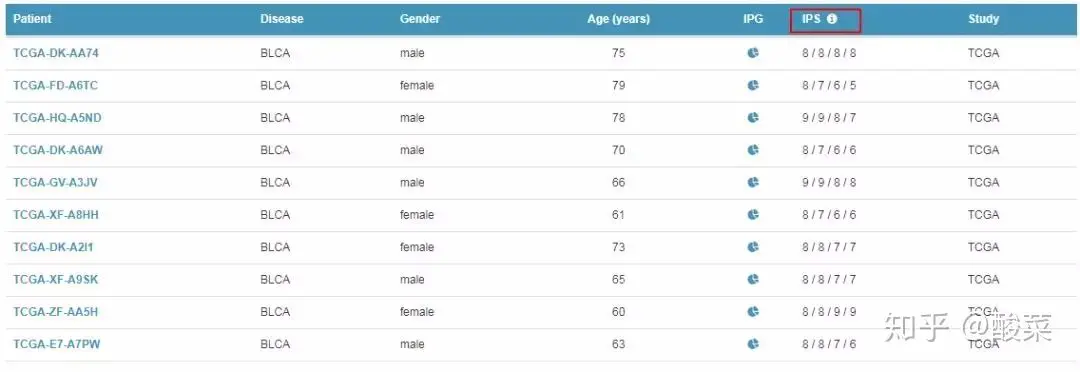
TCIA分别对每个病人进行分析,数据也提供下载,我们可以看到提供了ID、疾病、性别和年龄信息,我们重点关注IPS这一列的信息,IPS这一列有4个项目,有不同的属性,作者在文章中表示IPS(immunophenoscore) 可以很好的预测CTLA-4和PD-1反应性的预测因子。
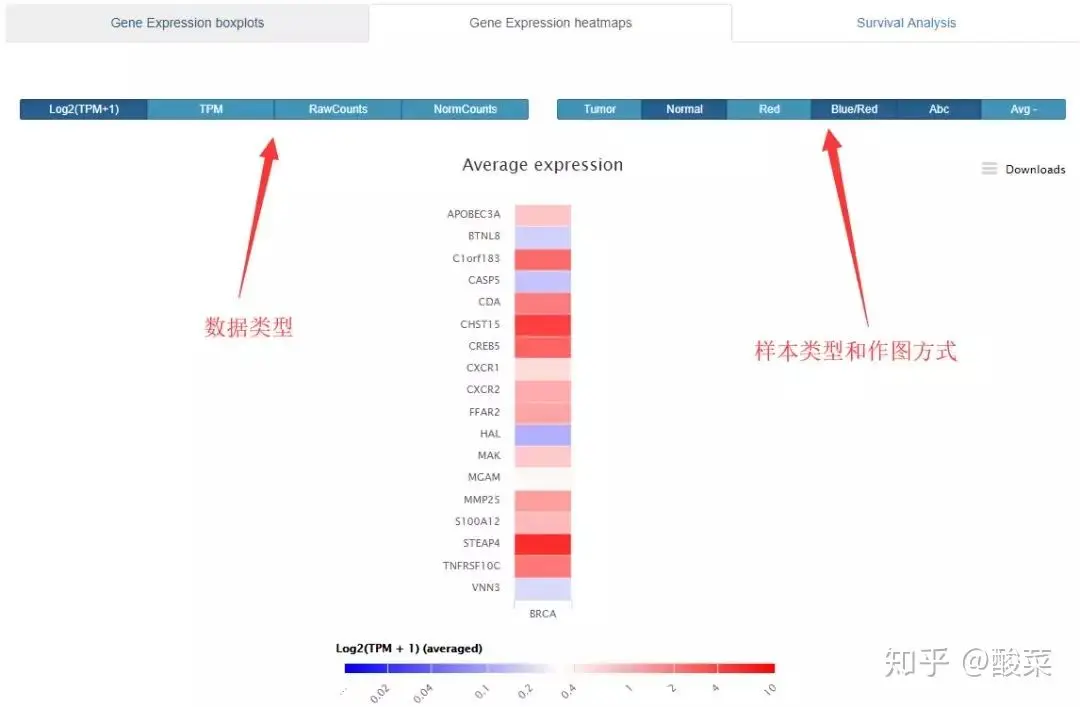
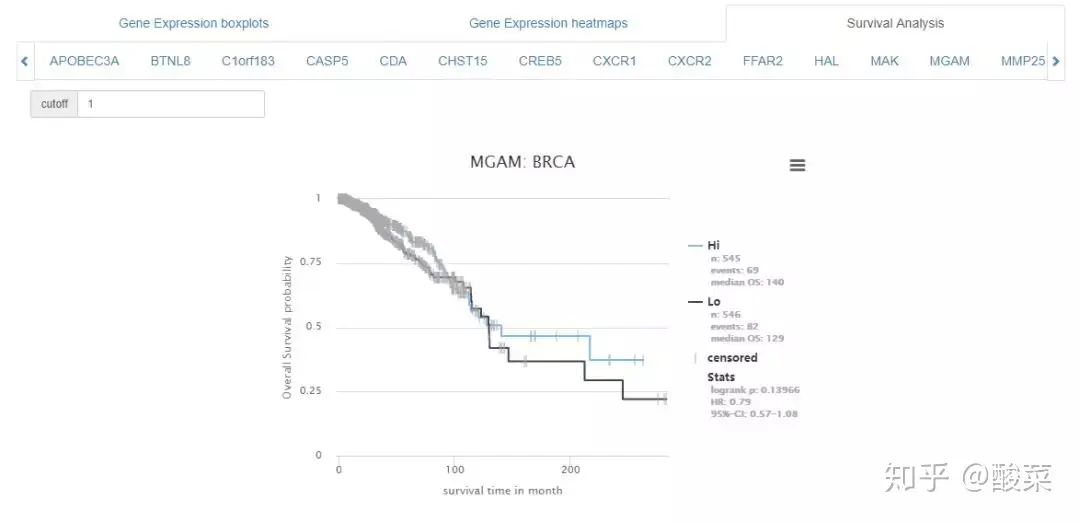
02 Gene Expression模块
在左侧的选择栏里筛选病人和基因后,可对单个基因进行差异分析和生存分析,值得注意的是这些基因都是和免疫相关的基因。笔者认为TCIA的这个模块并不怎么好用,也没有做检验,作图不怎么好看,不过如果只是看一看还是可以的。生存分析模块,TCIA是根据中位表达值分组进行的分析,提供HR和p值。

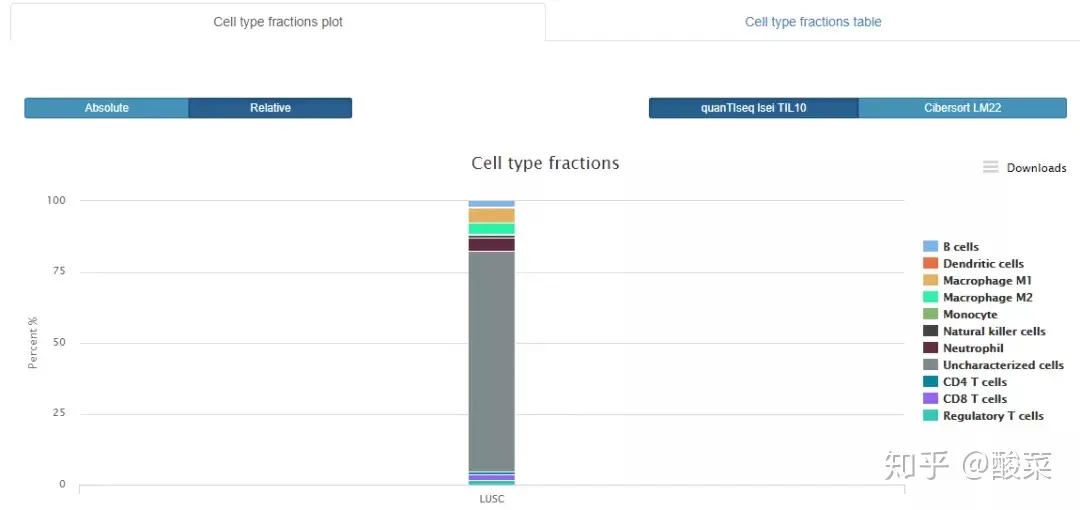
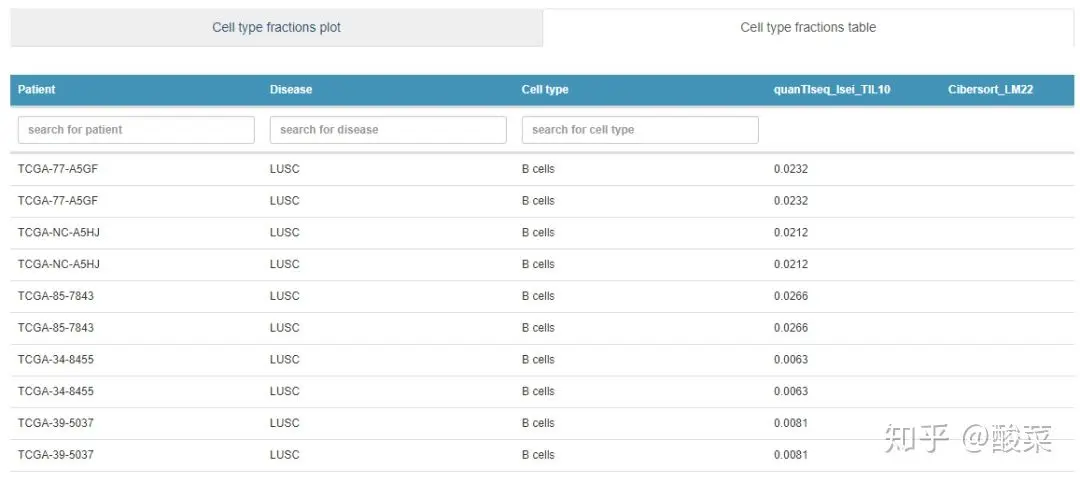
03 Cell Fractions
这个模块提供不同免疫细胞比例的展示,Absolute和Relative表示免疫细胞的绝对数和相对数,是CIBERSORT的不同计算方法结果,同时在table栏提供快捷的搜索。
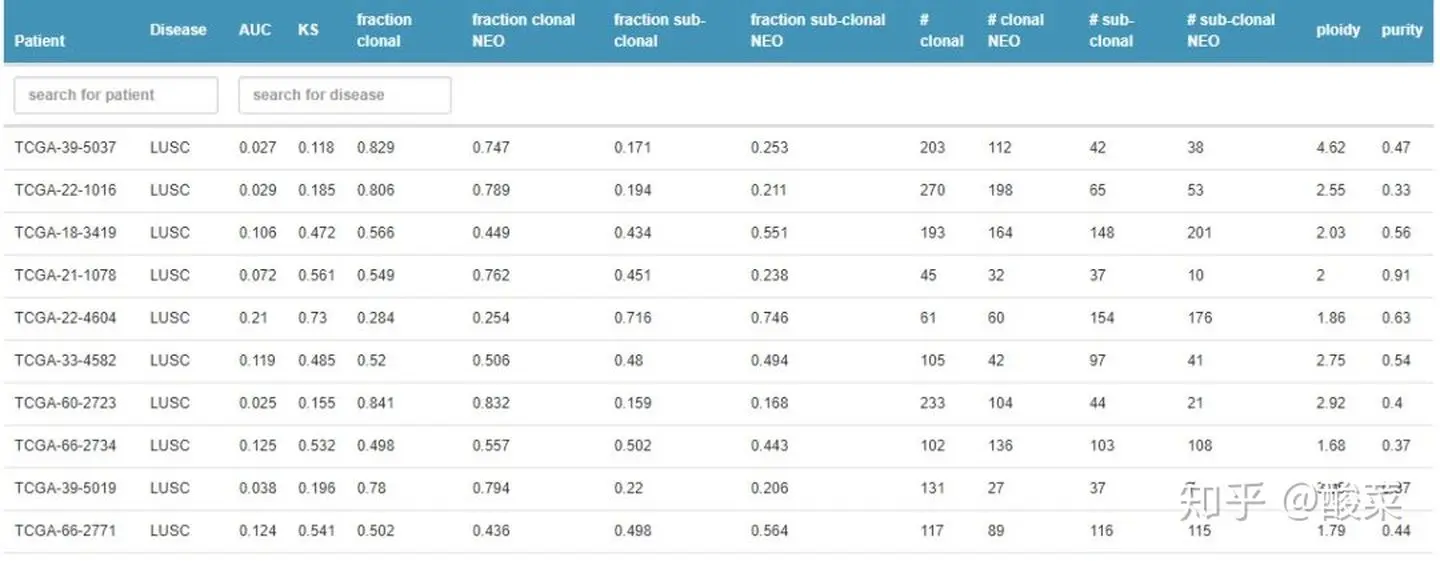
04 Heterogeneity
TCIA对每个样本的癌症抗原和遗传特征进行了分析,包括肿瘤异质性和克隆性,以方便分析免疫特征和肿瘤的遗传特征。
05 Neoantigens
这个模块提供疾病的突变数和突变压力展示,也提供展示预测到的新抗原结果。不过笔者也想说,这种新抗原预测,因为没有办法用实验的方法证伪,所以看看就好了,用作分析还是可以的,就看你的功力深厚了。

06 Tools模块
这个模块提供一个计算功能,可计算每个样本的免疫表型分数,只要提供一个标准的表达矩阵即可,不过值得提醒的是该工具要求表达数据要求用TPM方法定量的。
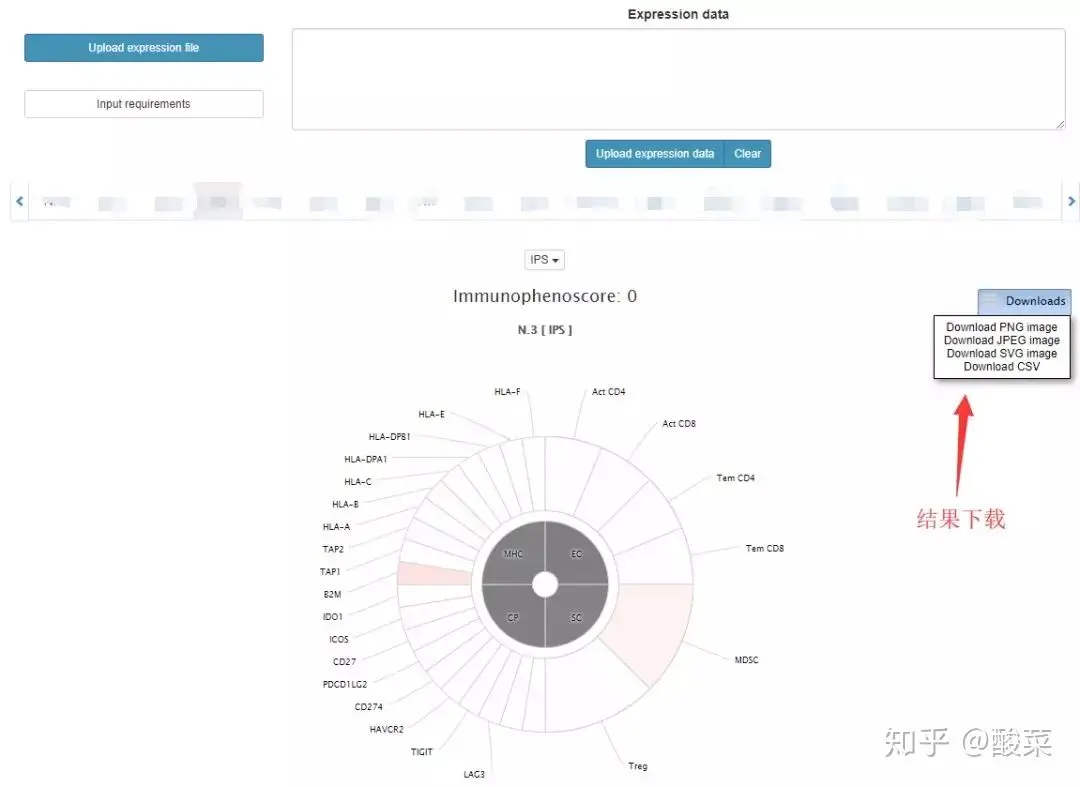
好了,这个数据库就介绍到这里。总结一下,这个数据库主要还是对TCGA的数据进行二次分析,得到的一些结果也可以辅助大家分析,同时提供的IPS计算也可给大家的NGS数据分析锦上添花,如果结果理想的话。
参考资料
- https://www.jianshu.com/p/077c4bde24f8
- Charoentong, P., Finotello, F., Angelova, M., Mayer, C., Efremova, M., Rieder, D., Hackl, H., Trajanoski, Z. (2016). Pan-cancer Immunogenomic Analyses Reveal Genotype-Immunophenotype Relationships and Predictors of Response to Checkpoint Blockade. Cell Rep. 2017. 18:248-262
